Zarski jp cyto,av,im 2014
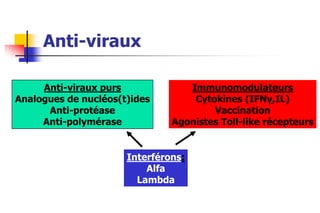
- 1. Anti-viraux Anti-viraux purs Analogues de nucléos(t)ides Anti-protéase Anti-polymérase Immunomodulateurs Cytokines (IFNγ,IL) Vaccination Agonistes Toll-like récepteurs Interférons: Alfa Lambda
- 2. Antiviraux Hépatite B Interféron α Analogues de: Nucléosides Nucléotides Hépatite C Interféron α Autres interférons Ribavirine Anti-protéases Anti-polymérase: NS5b Nucléosidiques Non nucléosidiques Anti-NS5a Inhibiteurs d’entrée Agonistes Toll-like récepteurs
- 3. INTERFERONS . Protéines ou glycoprotéines . Spécifiques de l’espèce . Agissant sur la cellule cible (récepteur) . Expression de certains gènes : synthèse des ARNm et protéines
- 4. INTERFERONS Caractéristiques IFN Cellules Structure Chromosome Inducteurs INF IFN Leucocytaire (lympho T et B macrophage) Fibroblastique Lympho T G20 Kda 165 AA GP 20 Kda 165 AA GP 17 Kda 146 AA 9 p 21 9 p 21 virus, virus, polyribonucléotides polyribonucléotides 12 Antigènes Mitogènes des lympho T
- 5. INTERFERONS Récepteurs . Spécifiques présent à la surface des cellules . et # . Haute constance d’affinité . Nombre de sites récepteurs faible
- 6. INTERFERON Récepteur / (IFNAR) + IFN IFN IFNAR2 IFNAR1 = 110 -130 Kd IFNAR2 = 55 - 95 Kd IFN IFNAR1 Intermédiaire
- 8. INTERFERON Mécanisme d’action P Tyk-2 STAT-1 STAT-1 STAT-1 STAT-2 P STAT-2 48 P P STAT IFN Jak-1 ISRE Tyk-2 et Jak-1 =Tyrosines kinases STAT S = facteurs de transcription ISRE = Interferon Sensitive Response Element
- 9. IFN and Type 1 IFNs ISGF: Interferon-Stimulated Genes Factor IRF: Interferon Regulatory Factor ISRE: Interferon Stimulated Response Element ISG: Interferon-Stimulated Genes
- 10. INTERFERONS 1°) Expression induite : - 2 ’5 ’ OAS - Protéine kinase, Mx - CMH I et II - Beta 2 microglobuline - Xanthine oxydase - Récepteur du TNF 2°) Expression inhibée - c-myc, c-fos - collagène
- 11. INTERFERON Action des principales enzymes induites : 1°) 2’ 5’ oligoadénylate synthétase : - catalyse synthèse d’oligomères d’adénine - oligomères activent endonucléase - destruction des ARN viraux 2°) Protéine kinase P1 - Sérine thréonine kinase - initiation de la synthèse protéique
- 12. INTERFERON ALPHA Effet immunomodulateur HLA II IFN Th0 IL12 rIL12 IFN Th1 Th2 Activation CTL IFN IFN HLA I NK Activation Cellule B Prolifération Anticorps IFN
- 13. INTERFERON ALPHA Effet anti-fibrosant In vitro et in vivo? ( TGF béta 1) Effet anti-oncogénique Direct: anti-prolifératif anti-oncogénique Indirect: protéines virales, immunomodulation, anti-fibrosant et anti-angiogénèse
- 14. CHARACTERISTIQUES DES IFN-PEG PEG-IFN 2a Taille: 40kDa Structure: branché Dose fixe Clairance hépatique PEG-IFN 2b Taille: 12kDa Structure: linéaire Dose adaptée au poids Clairance rénale
- 15. Antiviraux Hépatite B Interféron α Analogues de: Nucléosides Nucléotides Hépatite C Interféron α Autres interférons Ribavirine Anti-protéases Anti-polymérase: Nucléosidiques Non nucléosidiques Inhibiteurs d’entrée Agonistes Toll-like récepteurs
- 16. ADN VHB sous IFN-PEG a2a et séroconversion HBe ADN VHB moyen (log10 cp/ml) 12 10 Pas de séroconversion HBe à S72 (n = 184) 8 6 -3,8 log10 cp/ml Séroconversion HBe à S72 (n = 87) 4 10 000 cp/ml -5,84 log10 cp/ml 2 33 % Période de Survenue séroconversion HBe Suivi Traitement 29 % 38 % 0 0 12 24 36 48 60 2,30 log10 cp/ml Séroconversion HBe et HBs à S72 (n = 8) 72 Semaines EASL 2006 – T. Piratvisuth, abstract 49
- 17. MOLECULES ANTIVIRALES Analogues de nucléos(t)ides Guanine . Entécavir Adénine . Ara-MP Analogues fluorés . FIAU (Uracyl) Phosphonates de nucléosides acycliques . Adéfovir, Ténofovir Analogues de pyrophosphates . Foscarnet Analogues lévogyres de nucléosides . Lamivudine (Cytidine) . FTC ou Emtricitabine (Cytidine) . L-dT (Telbivudine) . LFD4C (Cytidine)
- 18. ANALOGUES DE NUCLEOSIDES Efficacité Bonne captation cellulaire Phosphorylation par les kinases cellulaires (triphosphate) Degré de compétition avec les nucléosides naturels endo-cellulaires Efficacité de la liaison à la polymérase virale et de son incorporation dans la chaine d ’ADN naissante
- 21. ENTECAVIR O Analogue de la guanine N Inhibiteur sélectif et puissant du VHB (EC50 = 4 nM, Ki = 1 nM) Agit à 3 niveaux de la polymérase: Initiation Synthèse ADN-dépendante Reverse transcription CH 2 OH OH N NH N NH 2
- 22. ENTECAVIR :ADN VHB Dosing 3,5 3 2,5 Placebo 0.05 mg 0.1 mg 0.5 mg 1.0 mg 2 1,5 1 0,5 0 0 1 2 3 Weeks 4 6 8
- 23. TENOFOVIR Analogue nucléotidique (monophosphorylé) Utilisé dans le VIH depuis 2000 Inhibe l’ADN Polymérase Terminateur de chaine Plus efficace que l’Adéfovir Aucune mutation de résistance à 6 ans Tolérance rénale bonne mais: Clairance à surveiller Hypophosphorémie
- 24. Réduction de l’ADN du VHB après 1 an de Traitement ADV1 10 mg ADV2 30 mg LAM3 LdT3 ETV4 TDF5 Réduction de l’ADN du VHB à 1 an (Log10) 0 -1 -2 -3 -4 -5 -6 -3,5 -4,8 -5,5 -6,5 -6,9 -6,4 -7 -8 Patients AgHBe-positifs *Données issues d’études indépendantes, ne permettant pas de comparaisons (populations différentes, valeurs initiales de charges virales et méthodes de quantifications de l’ADN du VHB différentes) 1Hepsera [RCP]; 2Marcellin et al., N Engl J Med 2003, 348: 808-16; 3Sebivio [RCP]; 4Baraclude [RCP]. 5Heathcote et al., AASLD 2007, abstract LB6; Fontana R.J., Gastroenterlogy 2009, 136(2):389-92.
- 25. MUTATIONS DE RESISTANCE Terminal protein 1 spacer 183 I(G) Pol/RT 349 (rt1) II(F) A LAM / FTC 692 (rt 344) GVGLSPFLLA B YMDD C L180M D E ETV T184G M204I/V A181V LdT 845 a.a. V173L ADV Allen Hepatology RNaseH N236T S202I M250V M204I 1998, Delaney J Virol 2003, Angus Gastroenterology 2003, Villeneuve J Hepatol 2003, Lai AASLD 2003, Colonno HepDart 2003
- 26. Résistance à 6 ans Année 1 Année 2 Année 3 Année 4 Année 5 Année 6 72 SEMAINES LVD1 23% 46% 55% 71% 80% – 0% 3% 11% 18% 29% – 5% 25% – – – – TDF§4 0% 0%§ 0% 0% 0% 0% ETV*5,6 <1% <1% 1.2% 1.2% 1.2% 1.2% ADV‡1 LdT†2,3 § Patients avec ADN VHB ≥400 copies/mL à S72 peuvent ajouter FTC au TDF; ainsi la résistanceau TDF monotherapie après 72 semaines ne peut pas être totallement certifiée5,6 * probabilité cumulée d’apparition de résistance; † AgHBe (+) naïf; ‡ AgHBe(-) Naïf; N/A non disponible 1. Locarnini S. Hepatol Int. 2008;2:147-51. 2. Lai CL, et al. N Engl J Med, 2007;357:2576-8; 3. Liaw YF, et al. Gastroenterology 2009;136:486-95. 4. Snow-Lampart A, et al. AASLD Oct 31–Nov 4, 2008, San Francisco, USA. Oral Presentation 977 Hepatology 2008;48:745A. 5. Baraclude EU SmPC, February 2009. 6. Tenney et al. EASL April 22–26, 2009, Copenhagen, Denmark, Oral
- 27. Très fréquent: 1/10 Expert Panel Italian Guidelines STI review 2009;2:14-27. fréquent: 1/100-1/1,000 Rare: 1/1,000-1/10,000 Entecavir Telbivudine Lamivudine Adefovir Tenofovir Très rare: >1/10,000 Amylase, lipase Peripheral neuropathy Myalgia, rhabdomyolyse CPK Pancreatite Nécrose tubulaire Cl Créatinine Thrombocyto penie Acidose lactique Hypophosph atemie Rash Dyspnée Malaise Céphalées Gastrointesti nal Vertige TOLERANCE
- 28. Antiviraux Hépatite B Interféron α Analogues de: Nucléosides Nucléotides Hépatite C Interféron α Autres interférons Ribavirine Anti-protéases Anti-polymérase: Nucléosidiques Non nucléosidiques Inhibiteurs d’entrée Agonistes Toll-like récepteurs
- 29. Cinétique de l‘ARN VHC 14 3 MU 5 MU 10 MU x 106 copies/mL 12 10 8 6 4 2 0 0 24 Hours 48 Lam et al., Hepatology. 1997;26:226-231
- 30. ARN VHC Effet de la Pégylation IFN TIW IFN + RBV PEG IFN Daily IFN 12 10 8 6 4 2 0 0 24 48 Temps
- 31. Cinétique virale: Apport de la ribavirine Feld et al, Gastroenterology 2010
- 32. 31 Cinétique virale en fonction du génotype de l’IL28B (génotype 1) Afro-américains Caucasiens 0 0 -2,0 -2,0 TT CT TT -4,0 CT -4,0 -6,0 CC -6,0 4 2 4 Hispaniques 12 Semaines 0 -2,0 TT -4,0 CT CC 4 2 4 12 Semaines La réduction de la charge virale est associée indépendamment au génotype de l’IL28B et à l’ethnie (p < 0,0001) CC -6,0 4 2 4 12 Semaines Thompson et al, Gastroenterology 2010
- 33. RIBAVIRINE Analogue nucléosidique de la purine Forme active: ribavirine triphosphate Effet anti-viral: Réplication virale: faible ( 0,3 Log) 2 ’5 ’ OAS en synergie avec l ’interféron Inhibition de l ’IMPDH Réduction de synthèse de GTP Mutations possibles (NS5b)
- 34. MECANISME D’ACTION DE LA RIBAVIRINE Glutamine PRA Ribavirine IMP (Inosine monophosphate) Ribavirine - MP XMP (Acide xanthylique) GMP, GDP, GTP
- 36. Un déficit génétique protégeant de l’anémie Permet de détecter ≈ 30% des patients présentant un risque négligeable de développer une anémie Aide à la décision clinique chez les patients à haut risque d’anémie
- 37. Inosine triphosphatase (ITPase) 2 variants fonctionnels Chromosome 20 Exon 2: rs1127354 Intron 2: rs7270101* Polymorphisme: diminution de Hb à S4 Allèle mineur protège * Non retrouvé au Japon Thompson et al, Gastroenterology 2010 Ochi et al, Gastroenterology 2010
- 38. Organisation du génome VHC et maturation de la polyprotéine 3’NCR 5’NCR Cadre de lecture TRADUCTION Protéines structurales Protéines non-structurales MATURATION Host signal peptide peptidase C Core E1 E2 Glycoprotéines d’enveloppe NS3/4A protéase NS2/3 protéase Host signal peptidase p7 NS2 Protéase NS3 Serine protéase 4A Hélicase CofacteurSeri ne protéase NS4B NS5A NS5B ARN-polymérase ARN-dépendante NCR : Non Coding Region Asselah T et al. Liver International 2009;29(s1):57-67.
- 40. Cibles Thérapeutiques NS3 Site de fixation du substrat de la protéase Site de fixation du substrat de la protéase Site catalytique de la protéase Site de fixation du zinc Site de fixation de NS4A Site d’attachement à la membrane de la protéase-hélicase Site de fixation du substrat de la protéase NS2/NS3 Pawlotsky JM, Chevaliez S, McHutchison JG, Gastroenterology 2007
- 41. Télaprévir : mode d’action Telaprévir Host signal peptide peptidase C Core E1 Host signal peptidase E2 Glycoprotéines d’enveloppe Inhibe le clivage de la polyprotéine NS3/4A protéase NS2/3 protéase p7 NS2 Protéase NS3 Serine protéase 4A Hélicase CofacteurSeri ne protéase NS4B NS5A NS5B ARN-polymérase ARN-dépendante • Télaprévir se lie à la protéase NS3A/4A empêchant la maturation de la polyprotéine NS et inhibant la réplication du VHC Adapté: Asselah T et al. Liver International 2009;29(s1):57-67.
- 43. RESISTANCE Inhibiteurs de protéase 36 Sauvage Telaprevir Boceprevir ITMN-191 54 155 156 Valine (V) Threonine (T) Arginine (R) Alanine (A) V36A/M T54A R155K/T 168 A156V/T T54A Aspartate (D) 170 A156S/T A156S/V Valine (V) V170A D168A/V/E Adapte de Kieffer et al. Hepatology. 2007;46(3):631-639. Graphic courtesy of Dr Ira M. Jacobson.
- 44. Les résistances TVR + PEG-IFN + RBV : Probabilité cumulative de perdre la détection du variant Variant* Temps médian de perte de détectabilité V36A/M 69 % (37/54) 36 semaines T54A 1,0 Patients ayant perdu la détection du variant avant la fin d’étude 86 % (12/14) 13 semaines R155K/T 60 % (36/60) 44 semaines 80 % (4/5) 24 semaines 54 % (22/41) 46 semaines 0,8 0,6 Médiane 0,4 NS3*36 NS3*54 NS3*155 NS3*156 V36M+R155K 0,2 0,0 0 10 20 30 40 50 Temps (semaines) 60 A156S/T/V 70 V36M+R155K * Variations non mutuellement exclusives. AASLD 2010 – D’après Kieffer TL et al., abstract LB11 actualisé.
- 45. Les nouvelles anti-protéases Siméprevir (Janssen) Danoprévir (Roche) Faldaprévir (Boehringer) MK-5172 (MSD) Asunaprévir (BMS) GS-9451 ABT-450 (Abbott) ACH-2684 (Achillion)
- 46. Les nouveaux anti-viraux directs Les anti-polymérases (NS5B) Nucléosidiques Sofosbuvir (Gilead) Méricitabine (Roche) Alios-2200 et-2158 (Alios) Non nucléosidiques Déléobuvir (Boehringer) Filibuvir Sétrobuvir (Roche) GS-9669 (Gilead) VX-222 (Vertex) ABT-333 et-072 (Abbott) Les anti-NS5A: Daclatasvir (BMS) Lédipasvir (Gilead) ABT-267 (Abbott)
- 47. La trithérapie avec IP 2ème génération: naifs génotype 1
- 48. Les molécules sont plus puissantes et vont plus vites: comparaison des 2 molécules MSD 100 90 80 70 60 50 40 30 20 10 0 PCR (-) à S12 96 69 S 12 Bocéprévir MK-5172
- 49. QUEST-1 : Trithérapie avec le Simeprevir chez les malades naïfs de génotype 1 Réponse virologique 100 p < 0,001 91 % 85 % 80 % Malades (%) 80 60 50% SMV + PR PR 40 20 210/264 0 65/130 RVS12 Population totale 224/264 TGR+ 203/224 RVS12 Jacobson I, USA, EASL 2013, Abs. 1425 actualisé
- 50. Siméprévir: patients en échec Etude ASPIRE (n=79) *PR:48 semaines (n=27) (n=69) (n=23) (n=51) (n=16) Lenz et al, EASL 2012
- 51. Cibles Thérapeutiques RdRp site NNI A site NNI C site NNI B site NNI D (Pawlotsky JM, Chevaliez S, McHutchison JG, Gastroenterology 2007;132:1979-98) Site catalytique
- 52. Inhibiteurs de la Polymérase Nucléosidiques: NS5b: Non nucléosidiques Analogues de substrats naturels NS5b: très conservée Tout génotype Haute barrière de résistance NS5a: Liaison à 1/5 sites allostériques Changement conformationnel du site catalytique Génotype spécifique Sélection de mutants
- 53. Inhibiteurs de la Polymérase Analogues nucléosidiques: NS5b Sofosbuvir, (Gilead) R7128 (Roche) BMS-790052 (BMS) IDX184 (Idenix) NS5a: Daclatasvir Lédipasvir Inhibiteurs non nucléosidiques GS-9190 (Gilead) PF-00868554 ou Filibuvir (Pfizer) ANA-598 (Anadys Pharmaceuticals) BI 207127 (Boehringer) VCH-916 et -222
- 55. NEUTRINO : PEG-IFN + RBV + Sofosbuvir pendant 12 semaines Réponse virologique Malades avec ARN VHC < LDQ* (%) 99 % 100 99 % 91 % 90 % 80 60 40 20 299/327 321/325 326/327 295/327 S2 S4 S12 Fin de traitement RVS12 0 * LDQ : ARN VHC < 25 UI/ml Lawitz et al, NEJM 2013
- 56. NEUTRINO : PEG-IFN + RBV + Sofosbuvir pendant 12 semaines RVS12 en fonction du génotype 100 96 % 90 % 89 % 295/327 261/292 27/28 Population totale Génotype 1* Génotype 4 100 % RVS12 (%) 80 60 40 20 7/7 0 *1a:92% 1b:82% Génotypes 5, 6 Lawitz E et al, NEJM 2013
- 57. Daclatasvir+Asunaprévir+PR chez les répondeurs nuls génotype 1 Réponse virologique 100 Patients (%) 100 90* 90 80 64 60 60 46 46 40 20 0 36 7 n = 11 6 5 9 5 10 11 10 11 S4 Groupe A : BMS-790052 + BMS-650032 S12 10 10 S24 Fin TTT 4 9 11 10 RVS Groupe B : BMS-790052 + BMS-650032 + PEG-IFNα/RBV *Un patient a eu un ARN < 25 UI/ml détectable au suivi S24 et était < 10 UI/ml (indétectable 35 jours après ) Lok A et al . N Engl J Med 2012; 366: 216-224.
- 58. Efficacité de la quadrithérapie chez les G1 répondeurs nuls ARN VHC < 25 UI/ml (%) 100 95 95 100 100 100 100 * 90 95 ASV 200 mg x 2/j + DCV + PEG/RBV 80 ASV 200 mg x 1/j + DCV+ PEG/RBV 60 Barres pleines < LDD (10 UI) 40 Barres hachurées Détectable et < LDQ (25 UI) 20 n= 0 75 71 20 21 S4 95 20 95 21 S12 * 2 patients ont rechuté : 1 à la semaine 4 90 20 100 90 95 21 20 21 S24 Fin traitement RVS 24 et 1 à la semaine 12 • G1 (88 % G1a), IL28B CT/TT (100 %) Lok A, Etats-Unis, AASLD 2012, Abs. 79 actualisé
- 59. Les associations sans interféron Bithérapie Trithérapie Quadrithérapie
- 61. Sofosbuvir + Daclatasvir (12 semaines) Malades avec ARN VHC < LDQ* (%) Réponse virologique 100 % 100 95 % 100 % 100 % 100 % 100 % 100 % 95 %** 91 % 80 % 80 60 DCV + SOF 40 DCV + SOF + RBV Manquant 20 0 n= 21 20 S2 21 20 S4 21 20 S24 21 20 RVS4 21 20 RVS12 ** Pas de donnée pour 1 malade à la visite suivi semaine 12 : ARN VHC était indétectable aux visites de suivi semaine 4 et semaine 24 (préliminaire) • Les 21 malades qui ont fait la visite de suivi semaine 24 ont tous un ARN VHC indétectable (RVS24) *LDQ : ARN VHC < 25 UI/ml Sulkowski M, USA, EASL 2013, Abs. 1417 actualisé
- 62. Sofosbuvir+Lédipasvir RVS 12 semaines SOF/LDV 97.7 97.2 SOF/LDV+RBV 94 93.1 SOF/LDV 93.6 SOF/LDV2 96.4 2 G1 naifs 12 semaines 8 semaines G1 prétraités Presse release
- 63. AVIATOR : ABT-450/r, ABT-267, ABT-333 +/- ribavirine - Génotype 1 RVS24 chez les malades naïfs par sous-groupes 100 92 94 98 91 94 94 89 95 91 89 RVS24 (%) 80 60 40 20 0 n= 78 81 108 50 35 124 113 42 115 44 Kowdley KV, USA, EASL 2013, Abs. 3 actualisé
- 64. AVIATOR : ABT-450/r, ABT-267, ABT-333 +/- ribavirine - Génotype 1 RVS24 chez les malades répondeurs nuls par sous-groupes 100 93 97 93 100 97 91 96 95 66 41 94 93 RVS24 (%) 80 60 40 20 0 n= 55 33 55 33 22 45 85 3 Kowdley KV, USA, EASL 2013, Abs. 3 actualisé
- 65. Et les génotypes 2 et 3?
- 66. FISSION : sofosbuvir + ribavirine versus PEG-IFN + ribavirine - Génotypes 2 et 3 Réponses virologiques PEG-IFN + RBV Patients avec ARN VHC < LQ (%) SOF + RBV 100 99 92 99 80 99 92 67 p < 0,001* 67 67 170/253 162/243 60 32 40 20 231/251 76/241 249/250 158/236 242/244 207/224 NA 188/190 0 S2 S4 S12 Traitement S24 S12 Suivi Gane E, Nouvelle-Zélande, EASL 2013, Abs. 5 actualisé
- 67. FISSION : sofosbuvir + ribavirine versus PEG-IFN + ribavirine - Génotypes 2 et 3 RVS12 selon le génotype et la présence d’une cirrhose PEG-IFN + RBV SOF + RBV 100 97 98 91 82 78 62 71 RVS12 (%) 80 63 56 61 60 34 30 40 20 68/70 52/67 58/59 44/54 10/11 8/13 102/183 110/176 89/145 99/139 13/38 11/37 0 Global Pas de cirrhose Génotype 2 Cirrhose Global Pas de cirrhose Cirrhose Génotype 3 Gane E, Nouvelle-Zélande, EASL 2013, Abs. 5 actualisé
- 68. FUSION : sofosbuvir + ribavirine 12 ou 16 semaines - Génotypes 2 et 3 Réponses virologiques Patients avec ARN VHC < LQ (%) SOF + RBV 12 semaines 100 87 81 98 97 SOF + RBV 16 semaines 100 100 p < 0,001 73 80 50 60 40 20 81/100 83/95 97/100 93/95 100/100 95/95 50/100 69/95 0 S2 S4 Fin de traitement Traitement S12 Suivi Nelson DR, USA, EASL 2013, Abs. 6 actualisé
- 69. FUSION : sofosbuvir + ribavirine 12 ou 16 semaines - Génotypes 2 et 3 RVS selon le génotype et la présence d’une cirrhose SOF + RBV 12 semaines 86 94 96 100 100 78 60 SOF + RBV 16 semaines 100 RVS12 (%) 80 60 40 40 20 61 63 62 80 60 p < 0,001 20 31/36 30/32 25/26 23/23 6/10 7/9 0 30 37 19 19/64 39/63 14/38 25/40 5/26 14/23 0 Global Pas de cirrhose Génotype 2 Cirrhose Global Pas de cirrhose Cirrhose Génotype 3 Nelson DR, USA, EASL 2013, Abs. 6 actualisé
- 70. POSITRON : sofosbuvir + ribavirine versus placebo – Génotypes 2 et 3 Patients avec ARN VHC < LDQ (%) Réponse virologique 100 99 % 100 % 91 % 78 % 80 60 40 20 186/205 202/204 202/202 161/207 0 S2 S4 S12 RVS12 RVS12 = 0 % dans le groupe placebo Jacobson I, USA, EASL 2013, Abs. 61 actualisé
- 71. POSITRON : sofosbuvir + ribavirine versus placebo – Génotypes 2 et 3 RVS12 en fonction du génotype et du stade de fibrose 100 93 % 94 % 92 % RVS 12 (%) 80 68 % 61 % 60 Total Pas de cirrhose Cirrhose 40 21 % 20 101/109 85/92 16/17 60/98 57/84 3/14 0 Génotype 2 Génotype 3 Jacobson I, USA, EASL 2013, Abs. 61 actualisé
- 72. Comparaison des études sofosbuvir et RBV chez les malades génotype 2 ou 3 Cirrhose G3 100 POSITRON FISSION FUSION RVS12 (%) 80 61 60 40 30 21 34 19 20 3/14 13/38 11/37 5/26 14/23 0 POSITRON : SOF + RBV 12 semaines FISSION : SOF + RBV 12 semaines FISSION : PEG-IFNα-2a + RBV 24 semaines FUSION : SOF + RBV 12 semaines FUSION : SOF + RBV 16 semaines Gane E, Nouvelle-Zélande, EASL 2013, Abs. 5 actualisé Jacobson IM, USA, EASL 2013, Abs. 61 actualisé Nelson D, USA, EASL 2013, Abs. 6 actualisé
- 73. Etude VALENCE : sofosbuvir chez G2/3 RVS12 chez patients G2 traités 12 semaines 100 97 100 91 RVS12 chez patients G3 traités 24 semaines 88 100 60 40 20 0 92 87 80 RVS12 (%) RVS12 (%) 80 94 60 60 40 20 29/30 2/2 30/33 7/8 Non cirrhotiques naïfs Cirrhotiques naïfs Non cirrhotiques déjà traités Cirrhotiques déjà traités 0 86/92 12/13 87/100 27/45 Non cirrhotiques naïfs Cirrhotiques naïfs Non cirrhotiques déjà traités Cirrhotiques déjà traités Zeuzem S, Allemagne, AASLD 2013, Abs. 1085, actualisé
- 74. Trithérapie courte Peg/RBV + sofosbuvir chez les génotypes 2 et 3 Pourcentage de réponse à S12 Absence de cirrhose Cirrhose 9/9 13/14 10/12 10/12 Résultats en intention de traiter (3 perdus de vus) 74 AASLD 2013 - D’après Lawitz E al., abstract LB4, actualisé
- 75. Inhibition de la cible cellulaire de l’hôte Inhibiteurs d’entrée virale (AC) 1. • • CD81? Scavenger récepteur BI (SR-BI) Inhibiteurs de la biosynthèse des lipides 2. • • Statines? Sécrétion des VLDL? Inhibiteurs de la cyclophiline B 3. • • Interagit avec la région C-terminale de NS5B Debio-025 Insulino-résistance Récepteurs nucléaires 4. 5. • • • PPAR Farnésoid X récepteur (FXR) Œstrogène récepteur (ESR)
- 76. Inhibiteurs de la cyclophiline Débio 025*: Alisporivir *Interagit avec NS5b, sans propriétés anti-calcineurine Per os
- 77. Inhibiteurs de la cyclophiline Débio 025*:Alisporivir Flisiak et al, Hepatology 2009
- 78. Antiviraux Hépatite B Interféron α Analogues de: Nucléosides Nucléotides Hépatite C Interféron α Autres interférons Ribavirine Anti-protéases Anti-polymérase: Nucléosidiques Non nucléosidiques Inhibiteurs d’entrée Agonistes Toll-like récepteurs