Claseteoricasemana2
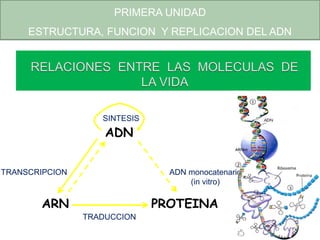
- 1. ADN ARN PROTEINA TRANSCRIPCION ADN monocatenario (in vitro) TRADUCCION SINTESIS PRIMERA UNIDAD ESTRUCTURA, FUNCION Y REPLICACION DEL ADN
- 3. QUIMICA ADN Y ARN son polímeros lineales compuestos de monómeros de nucleótidos (polirribonucleótido) asociada a proteínas (observación en los cromosomas). ESTRUCTURA Modelo propuesto por Watson y Crick (1953): Patrones de difraccion de R-X Macromolécula formada por dos cadenas, 4 desoxirribonuclótido Cadenas antiparalelas y complementarias: Tamaño, forma y comp. química Implicancia: 1. Proporción de A igual a T, y G igual a C 2. Proporción de bases púricas (A+G) igual a pirimidinas (T+C) Estructura responde a: 1. Duplicación exacta de la moléc. Un cadena sirve como molde para la síntesis de la otra 2. Separación de ambas cadenas (denaturación) y reunión de dos cadenas complementarias (renaturación) puede tener origines diversos. 3. Almacena un mensaje, codificado en la variación de secuencia de bases (código genético) 4. Gran estabilidad, con algunos cambios (mutación)
- 4. TIPOS DE MOLÉCULA Procariotas y eucariotas con doble cadena, circulares y lineales Virus: 1. ADN de doble cadena. Ejm. Fagos T 2. ADN de cadena sencilla. Ejm. Fago ΦX174 3. ARN de doble cadena. Ejm. Virus de la gripe 4. ARN de cadena sencilla. Ejm. TMV FUNCIONES Transcripción : moléc. Informativa (ARNm), funcionales (ARNr, ARNt) Traducción: ARNpol lee el ADN en sentido 3’ 5’, síntesis ARNm 5’3’ Organismo superiores: ARNnp (ARN nucleolar); ARNcp (ARN citoplasmático) Información almacenada en tripletas de bases: Código Genético 1. Se lee de manera continua cada tres bases: Tripleta 2. Degenerado, un aa codificado por mas de un 1 triplete 3. Tripletas de inicio (AUG,etc) y tripletas stop (UAA; UAG; UGA) Los aa incorporados a la proteína queda con extrema amino libre
- 5. Azúcar: Pentosa. -OH en C-2 de la ribosa mayor estabilidad química para función de catalisis Adenina Guanina Uracilo Timina Citocina PURINAS: mayor tamaño PIRIMIDINAS: menor tamaño Azúcar: pentosa Bases nitrogenada: compuestos heterocíclicos de nitrógeno y carbono. Grupo fosfato: da el carácter ácido a los ac. nucleicos. El fósforo se disocia en el pH intracelular liberando iones H.
- 7. Derivado de Pirimidina Derivado de Imidasol Enlace Fosfodiéster Enlace β-N-Glucosidilo Posición “SIN” “ANTI” Nucleósido: azúcar + base. Ejm. Adenosina (A), Desoxiadenosina (dA), etc. Nucleótido: azúcar + base + fosfato. Ejm.: Adenosina trifosfato (ATP), Desoxiadenosina trifosfato (dATP), dGTP, dCTP, dUTP. Las células y líquidos extracelulares tienen pequeñas cantidades de nucleósidos. Conformación SIN
- 9. DESNATURACION o “FUSION” DEL ADN EN FUNCIÓN DE LA % DE GC GC mayor T° de desnaturalización AT menor T° de desnaturalización Produce: La viscosidad se reduce Aumento Absorción de UV La densidad aumenta
- 12. COMO SE PUEDE DEMOSTRARA QUE EL ADN ES EL MOLECULA DE LA VIDA???
- 13. EXPERIMENTO DE FREDRERICK GRIFFITH (1928) TRANSFORMACION BACTERIANA EL NUCLEO ESTA COMPUESTO POR EL ADN Y PROTEÍNAS??? CUAL MOLÉCULA ES PRODUCE LA VIDA???
- 14. OSWALD AVERY COLIN McLEOD MACLYN McCARTY (1944) LA SUBSTANCIA TRANSFORMANTE DE LAS CELULAS R EN S ES EL ADN
- 15. DOBLE HELICE
- 16. MOLECULAR STRUCTURE OF NUCLEIC ACIDS JD Watson, FHC Crick, Nature N°4356: 737-738 (April 1953) 1. Molécula de dos cadenas, girando sobre el mismo eje 2. Grupos fosfatos se unen al azúcar mediante enlace fosfodiéster 3’,5’ 3. Las cadenas giran de derecha a izquierda alrededor del eje, con los átomos de ambas cadena en dirección opuesta. 4. Los nucleótidos (bases) están dentro del eje y el grupo fosfato por fuera 5. El azúcar se ubica mas o menos perpendicular a las bases 6. Existe ángulo 36° entre cada base; hay un base cada 3.4A°. Cada giro implica 10 bases, 34A°. 7. La distancia del átomo de fósforo al eje es 10A°. 8. Ambas cadenas están unidas por una purina y pirimidina, unidas mediante enlace de hidrogeno. Las bases están perpendicular al eje. 9. Enlaces de hidrogeno: posición 1 de purina ante posición 1 pirimidina; posición 6 de purina ante posición 6 pirimidina 10. El azúcar ribosa cambia a desoxirribosa por incorporación de un oxigeno extra
- 17. Unión de las cadenas polirribonucleótidos en la molécula de ADN La polimerización de los nucleótidos se da entre grupo hidroxilo del 3C y grupo fosfato del sgte de nucleótido: enlace ester (rx condensación). Puentes de hidrógeno Interacción hidrofóbica (entre bases) Fuerzas de van der Waals (entre bases) POSICION ANTI
- 18. HENDIDURA MENOR HENDIDUR A MAYOR 2.4 nm 3.4 nm. 10.5 nt. DEXTRÓGIRA LEVÓGIRA
- 19. FORMA B: hélice de Watson y Crick. FORMA A: ADN B hidratada. Moléc. compacta. 11 nt./vuelta. Bases apiladas e inclinadas al eje fosfato/azúcar. Se da entre ADN-ADN; ADN-ARN. FORMA Z: Eje azucar-fosfato en ZIG-ZAG. 12 nt./vuelta. Configuración “SIN” y “ANTI” del -N-Glucosídico. es 1.8 nm. Vuelta de 4.6 nt. Secuencia CG expuestas por enlace “SIN”. Conformación levógira. TRIPLE HELICE: secuencias A y G de una hebra se aparea con T y C de moléc. (apareamiento HOOGSTEEN) ADN. Solo en In vitro o reparación o recombinación del ADN,.
- 21. MOD ELOS D E R EPLIC AC IÓN D EL AD N 1. Replicación Conservativa 2. Replicación Dispersiva 3. Replicación Semiconservativa Experimento de Meselson y Sthal: N14 (ligero) N15 (pesado). E. coli. Experimento de Taylor etal. F. fava. Tritio radiactivo.
- 23. MOD OS D E REPLICACION
- 24. Único Origen de Replicación Unidireccional Replicación círculos rodantes Corte de una hebra de la doble hélice En el extremo 3-OH se se agregan los nucleótidos El extremo 5-fosfato se desplaza del molde La horquilla replicación puede girar varias, muchas moléculas REPLICACION EN VIRUS Y ALGUNOS PLASMIDOS
- 25. Replicación theta ( Jhon Cairns, 1963) Único Origen de Replicación Replicación bidireccional REPLICACION EN BACTERIAS
- 26. Cuando las moléculas de ADN circular se replican se observan lo que se denominan "ojos o burbujas" de replicación. La forma que adoptan los intermediarios de la replicación se parece a de la letra griega θ. Burbuja Forma θ
- 27. REPLICACION EUCARIOTAS Replicación en D. melanogaster varios orígenes Múltiples replicones
- 29. Para demostrar que la replicación es bidireccional se pueden realizar experimentos que se denominan de pulso y caza, en los que la célula es expuesta durante un breve periodo de tiempo en un medio con Timidina tritiada TH3 (pulso) y después se pasa a un medio con Timidina no radiactiva (fría) en exceso (caza). Posteriormente se extiende el ADN se un portaobjetos y después se realiza una autorradiografía. Replicación bidireccional
- 30. PROTEÍNA N O DNAB Capacita a la primasa para comenzar la duplicación PRIMASA Sintetiza el ARN cebador HELICASAS Desdobla la doble hélice. PROTEÍNAS SSB Estabiliza regiones de hebra simple. ADN GIRASA Introduce giros a la superhélice. ADN POLIMERASA III Sintetiza el ADN. ADN POLIMERASA I Saca el cebador y completa la síntesis. ADN TOPOISOMERASA I Corta una hebra de ADN. ADN TOPOISOMERASA II Corta ambas hebras de ADN. ADN LIGASA Une los extremos de los polinucleotidos preformados. MOLECULAS QUE PASTICIPAN EN LA REPLICACION DE E. coli
- 31. MECANISMO DE REPLICACION EN BACTERIAS INICIACION Unión de las proteínas de iniciación en Ori C. Se abre la doble hélice. DESENROLLAMIENTO ADN hélica rompe los puentes de H. Proteínas de unión a cadena simple (SSB). Forma tetrámeros que cubren 35-65 nucleótidos. ADN girasa, topoisomerasa, rompe una hebra de la hélice. Disminuye el superenrollamiento. CEBADORES La enzima primasa sintetiza los cebadores de ARN. Proporciona extremo 3-OH. ELONGACION Enzima ADN polimerasa. ADN ligasa.
- 32. Ori C en E. coli
- 34. REPLICACION SIMULTÁNEA Y EN DIRECCION OPUESTA
- 35. DIRECCIÓN DE SÍNTESIS DE ADN Cadena de Replicación Continua o Líder (3’ 5’) Cadena de Replicación Discontinua o Retrasada (5’ 3’)
- 37. ADN POLIMERASAS BACTERIANA ADN POLIMERASA I Primera enzima identifica su actividad biológica (1969) Función principal eliminar cebador y reparación del ADN dañada por agente físicos Función secundaria es síntesis de ADN. Dar fidelidad a la síntesis DeLucia y Cairns descubren mutantes de E. coli para deficiencia de ADN pol I. ADN pol II Síntesis reparadora del ADN dañado por agentes externos físicos y reinicia la replicación. (ADNpol IV, V reparan el ADN) Actividad Exonucleasa 3’ 5’ Prueba de corrección de la síntesis La enzima polimeriza en una dirección y a la vez escindir los nucleótidos Actividad Exonucleasa 5’ 3’ Escindir los nucleótidos del extremo donde inicio la síntesis Eliminar los cebadores
- 38. ADN pol III Subunidades Función Polimerización Exonucleasa 3´5´ ¿? Cargar la enzima en el molde ’ Abrazadera β Abrazadera corrediza Dimeriza el complejo Nuclear NUCLEO ENZIMATICO COMPLEJO Holoenzima, formada por dos subunidades de 10 péptidos cada una
- 47. DUPLICACIÓN DEL ADN EN EUCARIONTES Y PROCARIONTES En los eucariontes, cada uno de los numerosos cromosomas contiene molécula muy larga lineal de DNA. Los procariontes son diferentes ya que ellos, requieren únicamente dos horquillas de duplicación a una sola burbuja. Esto es cuestión de velocidad. En los eucariontes son esenciales muchos sitios de duplicación debido a que los complejos de duplicación trabajan mucho más lentamente que en los procariontes. En procariontes, la mayoría de DNA es una sola molécula circular que no es tan larga como una molécula de DNA de eucariontes (aprox. 1 400 veces mas DNA por célula que una bacteria).