ALINEAMIENTO DE SECUENCIAS BIOINFORMATICA
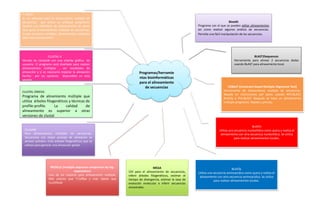
- 1. Programas/herramie ntas bioinformáticas para el alineamiento de secuencias Bioedit Programa con el que se pueden editar alineamientos así como realizar algunos análisis de secuencias. Permite una fácil manipulación de las secuencias. BLAST2Sequences Herramienta para alinear 2 secuencias dadas usando BLAST para alineamiento local. COBALT (Constraint based Multiple Alignment Tool) Herramienta de alineamiento múltiple de secuencias. Basada en restricciones por pares usando RPS-BLAST, BLASTp y PHI-BLAST. Después se hace un alineamiento múltiple progresivo. Rápido y preciso. MEGA Útil para el alineamiento de secuencias, inferir árboles filogenéticos, estimar el tiempo de divergencia, estimar la tasa de evolución molecular e inferir secuencias ancestrales. MUSCLE (multiple sequence comparison by log- expectation) Uno de los mejores para alineamiento múltiple. Más preciso que T-Coffee y más rápido que CLUSTALW. ClustalW Para alineamientos múltiples de secuencias. Secuencias con mejor puntaje de alineación se alinean primero. Crea árboles filogenéticos que se utilizan para generar una alineación global . BLASTn Utiliza una secuencia nucleotídica como query y realiza el alineamiento con otra secuencia nucleotídica. Se utiliza para realizar alineamientos locales. BLASTp Utiliza una secuencia aminoacidica como query y realiza el alineamiento con otra secuencia aminoacidica. Se utiliza para realizar alineamientos locales. CLUSTAL OMEGA Programa de alinemiento múltiple que utiliza árboles filogenéticos y técnicas de profile-profile. La calidad de alineamiento es superior a otras versiones de clustal. CLUSTAL X Versión de clustasW con una interfaz gráfica de ususario. El programa está diseñado para realizar alineamientos múltiples , ver resultados de alineación y si es necesario mejorar la alineación facilita por las opciones disponibles en esta versión. T COFEE es un software para el alineamiento múltiple de secuencias que utiliza un enfoque progresivo. Genera una biblioteca de alineamientos de pares para guiar el alineamiento múltiple de secuencias. Puede combinar, también, alineamientos múltiples obtenidos previamente
