Tema 12
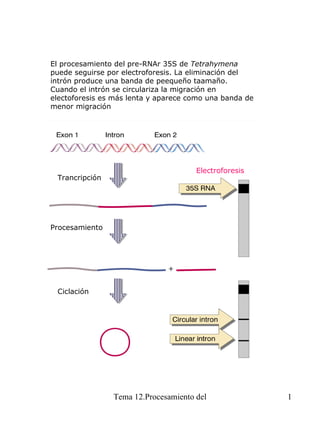
- 1. El procesamiento del pre-RNAr 35S de Tetrahymena puede seguirse por electroforesis. La eliminación del intrón produce una banda de peequeño taamaño. Cuando el intrón se circulariza la migración en electoforesis es más lenta y aparece como una banda de menor migración Trancripción Electroforesis Procesamiento Ciclación
- 2. El autoprocesamiento ocurre por sucesivas reacciones de transesterificación en las que los enlaces se intercambian directamente. Los enlaces generados en cada etapa aparecen s0mbreados Primera transfere n cia El extremo 3’0H de G ataca el extremo 5’ del intrón Segunda tra n sfere n cia El extremo 3’OH del exón A ataca el 5’ del exón B Tercera transferencia El extremo 3’OH del intrón ataca un enlace a 15 bases del extremo 5’
- 3. El intrón liberado puede formar círculos usando cualquiera de dos sitios internos para reaccionar con el extremo 5’. Los círculos pueden reabrirse por una reacción con agua u oligonucleótidos ataca Circularización Productos de circularización Circularización reversa Circularización secundaria Productos linearizados Reacción en trans
- 4. Los intrones del grupo I tienen una estructura común que esta formada por 9 regiones de bases apareadas. Las secuencias de las regiones P4 y P7 están conservadas e identifican elementos individuales de secuencia, P,Q, R y S. P1 se origina por apareamiento entre el extremo del exón izquierdo y el IGS del intrón. Una región entre P7 y P9 aparea con el extremo 3’ del intrón Primera transferencia Apareamiento de 2 pb en el extremo 3’ del intrón
- 5. El autoprocesamiento se puede ensayar en E. coli colocando el intón de Tetrahymena dentro de la secuencia de -galactosidasa. La síntesis de la enzima se prueba añadiendo un compuesto que se vuelve azul al ser metabolizado. Toda la secuencia está insertada en un fago y la presencia de placas azules indica procesamiento correcto Intrón insertado Transcripción Procesamiento Traducción -galactosidasa Placas azules indiacan expresión de -galactosidasa
- 6. Las reacciones catalíticas de la ribozima implican transesterificación entre un grupo en el lugar de unión a sustrato y un grupo en el lugar de unión a G Endorribonucleasa específica de secuencia Ligasa de RNA Fosfatasa
- 7. Las reacciones catalizadas por RNA tienen las mismas características que las catalizadas por proteínas aunque sus tasas son más lentas. La Km da la concentración del sustrato requeirida para la mitad de la velocidad máxima; es inversa de la afinidad de la enzima por el sustrato. La tasa de cambio (turnover) da el número de moléculas de sustrato transformadas por unidad de tiempo por un único sitio catalítico
- 8. El procesamiento por corte y empalme (nuclear) y el de intrones tipo II implica la formación de estructuras secundarias similares. Las secuencias implicadas en el primero son más específicas; el de intrones tipo II utiliza las posiciones que pueden ser ocupadas por purinas (R) o pirimidinas (Y) El procesamiento nuclear crea un centro activo por apareamiento entre U6-U2 y U2-intrón El procesamiento tipo II crea un centro activo por apareamiento de bases en los dominios 5 y 6
- 9. En tres tipos de procesamiento están implicadas dos reacciones de transesterificación. En la primera, un grupo OH libre ataca la unión exón 1-intrón. En la segunda, el OH creado en el extremo del exon 1 ataca la unión intrón-exón 2.
- 10. El procesamiento ocurre normalmente sólo en cis entre exones de la misma molécula de RNA, pero el procesamiento en trans puede ocurrir si se produce apareamiento entre intrones Procesamiento normal en cis Procesmiento en trans si existen secuencias complementarias en los intrones Productos del procesamiento en cis Productos del procesamiento en trans
- 11. Un intrón codifica para una endonucleasa que produce una rotura en la doble hélice. La secuencia del intrón se duplica y se inserta en la rotura Sitio diana endonucleasa Rotura en la diana El intrón copiado se introduce en la diana
- 12. La secuencia del gen de apoliproteína-B es la misma en intestino e hígado pero la secuencia del RNAm se modifica por un cambio de base que origina un codón de terminación en intestino Gen de apoliproteína-B con 29 exones Codón 2153 codifica para glutamina Edición RNAm en hígado codifica una proteína de 4563 aminoácidos RNAm en intestino origina una proteína de 2153 aminoácidos
- 13. La edición de RNAm ocurre cuando una desaminasa actúa sobre una adenina en una región de RNA duplexo imperfectamente apareado
- 14. El RNAm del gen coxII de tripanosoma tiene un cambio de cuadro con respecto al DNA. El cuadro correcto se crea por inserción de cuatro uridinas Codificado en el genoma Secuencia de DNA Cambio de cuadro Secuencia de RNAm Secuencia de la proteína
- 15. Parte de la secuencia del RNAm de coxIII de tripanosoma mostrando muchas uridinas que no están codificadas en el DNA (en rojo) o que han sido eliminadas del RNAm (T)
- 16. Apareamiento entre el RNA pre-editato y un RNA guía a ambos lados de la región a editar. El RNA guía proporciona un molde para la inserción de uridinas. El RNAm modificado por las inserciones es complementario al guía genoma RNA pre-editado Transcripción Apareamiento con guía RNA pre-editado RNA guía Inserción de uridinas RNA m RNAguía Liberación de RNAm RNAm
- 17. El genoma de Leishmania contiene genes que codifican para RNA pre-editados interpuestos con unidades que codifican los RNAs guías necesarios para producir las secuencias correctas de RNAm. Algunos genes tienen múltiples RNAs guías RNAs guía Genes
- 18. La adición o deleción de uridinas ocurre por roturas del RNA, incorporación o eliminación de uridinas y unión de los extremos.Las reacciones son catalizadas por un complejo enzimático bajo la dirección del RNA guía Endonucleasa Uridil transferasa terminal Ligasa de RNA