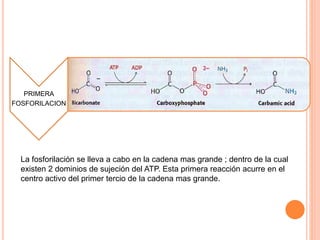
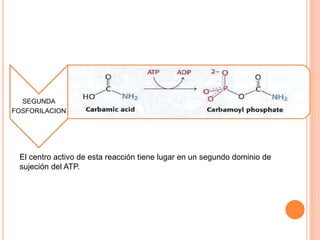
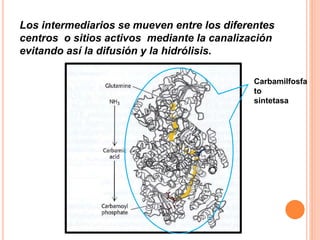
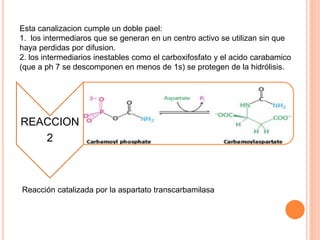
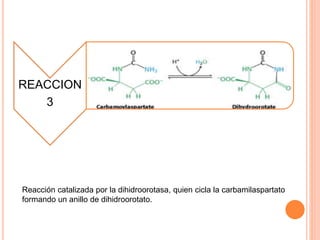
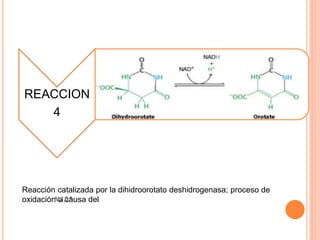
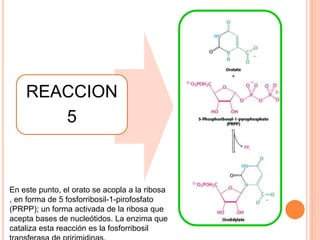
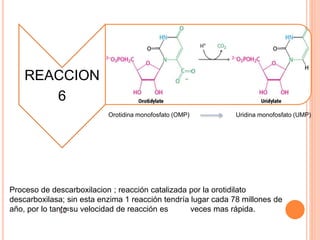
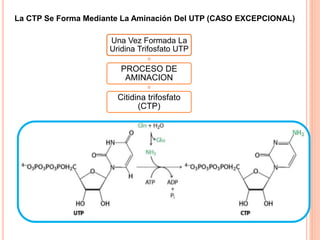
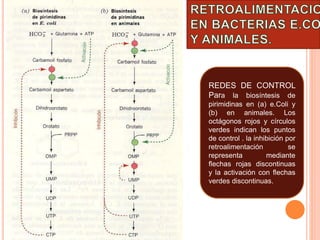
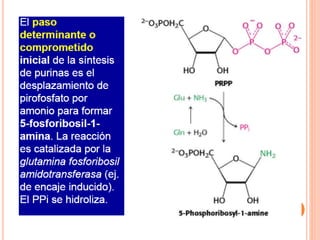
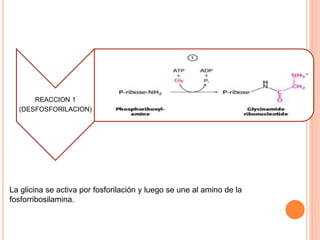
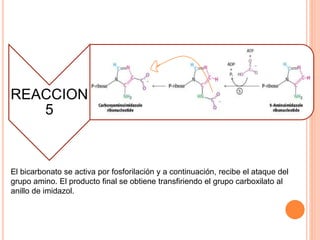
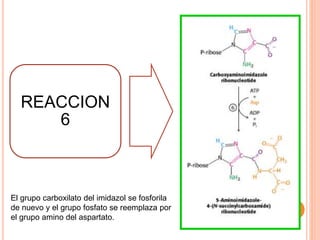
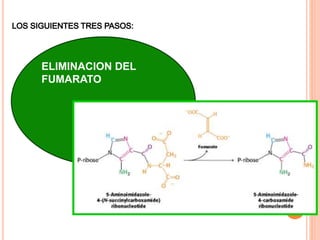
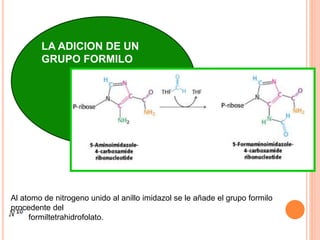
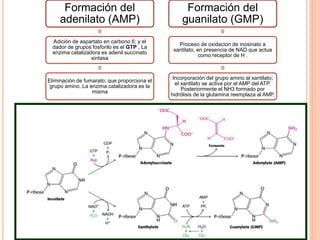
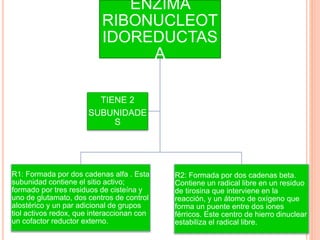
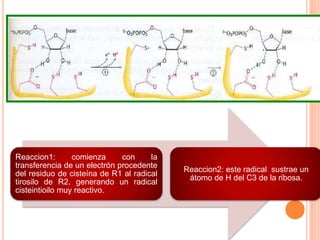
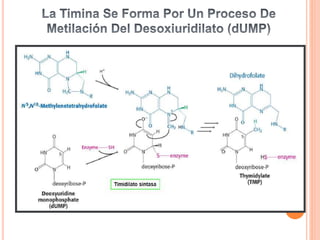
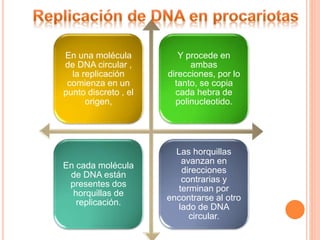
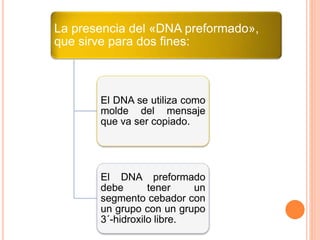
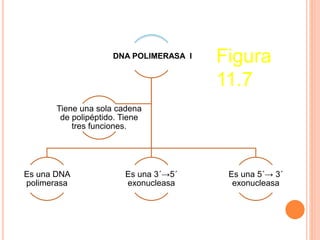
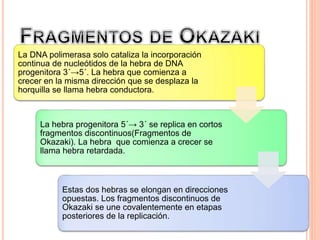
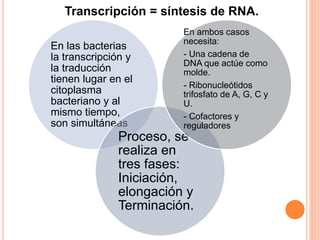
El documento describe la biosíntesis de nucleótidos a través de dos vías: la vía de novo y la vía de salvamento. Explica los pasos de la síntesis de las bases pirimidínicas y púricas, incluyendo las enzimas y reacciones involucradas. También cubre la replicación del ADN, describiendo su mecanismo semiconservador y los procesos de iniciación, progresión y terminación de la replicación.