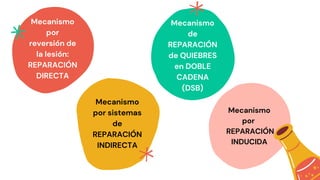
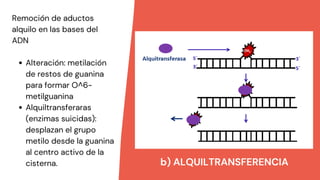
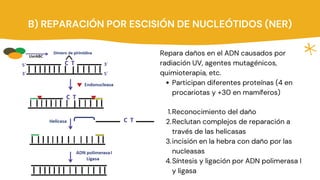
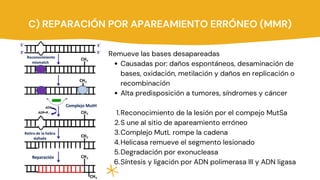
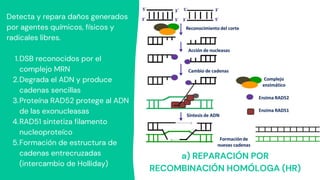
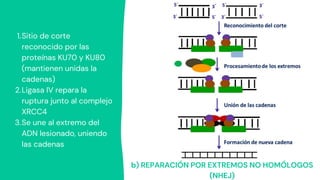
Los principales mecanismos de reparación del ADN incluyen la reparación directa, la reparación indirecta y la reparación de quiebres de doble cadena. La reparación directa involucra una sola enzima que repara las lesiones sin sustituir las bases dañadas, mientras que la reparación indirecta elimina los errores usando la cadena complementaria como molde. Los mecanismos de reparación de quiebres de doble cadena son la recombinación homóloga y la recombinación de extremos no homólogos. Además, la