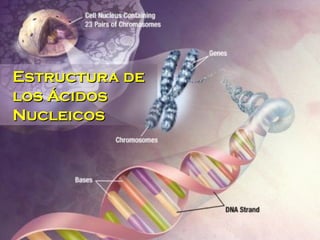
ACIDOS NUCLEICOS
- 1. Estructura deEstructura de los Ácidoslos Ácidos NucleicosNucleicos
- 2. James Watson y Francis CrickJames Watson y Francis Crick
- 7. Según su composición química, los ácidos nucleicos seSegún su composición química, los ácidos nucleicos se diferencian de las proteínas por su mayor contenido dediferencian de las proteínas por su mayor contenido de fósforo (10%) y por la ausencia de azufre.fósforo (10%) y por la ausencia de azufre. Dos tipos de ácidos nucleicos: ADN, ARN.Dos tipos de ácidos nucleicos: ADN, ARN. Localización y función.Localización y función. EucariotasEucariotas ProcariotasProcariotas VirusVirus ADNADN Núcleo CelularNúcleo Celular Matriz mitocondrialMatriz mitocondrial Estroma deEstroma de cloroplastoscloroplastos Zona nucleoideZona nucleoide CápsideCápside Depositario yDepositario y transmisor de latransmisor de la información genéticainformación genética organizada en genesorganizada en genes que codificanque codifican productos génicosproductos génicos ARNARN MomentáneamenteMomentáneamente en Núcleoen Núcleo Matriz mitocondrialMatriz mitocondrial CitosolCitosol CápsideCápside Transmisión deTransmisión de información bénticainformación béntica desde el ADN hasta losdesde el ADN hasta los productos génicosproductos génicos
- 8. DNADNA (ácido desoxirribonucleico)(ácido desoxirribonucleico) RNARNA (ácido ribonucleico)(ácido ribonucleico) Ácidos NucleicosÁcidos Nucleicos Cada monómero de ácido nucleico es un nucleótido formado por la unión de Ácido fosfórico Pentosa (ribosa o desoxirribosa) Bases nitrogenadas
- 9. DNA Y RNADNA Y RNA Pentosas - FisherPentosas - Fisher
- 10. Ribosas - HaworthRibosas - Haworth ββ-D-ribofuranosa-D-ribofuranosa ββ-D-2--D-2- desoxirribofuranosadesoxirribofuranosa
- 11. RibosasRibosas
- 12. DNA Y RNADNA Y RNA Las Bases NitrogenadasLas Bases Nitrogenadas BASES PÚRICASBASES PÚRICAS ADENINA (A)ADENINA (A) (DNA Y RNA)(DNA Y RNA) GUANINA (G)GUANINA (G) (DNA Y RNA)(DNA Y RNA) BASESBASES PIRIMÍDICASPIRIMÍDICAS CITOSINA (C)CITOSINA (C) (DNA Y RNA)(DNA Y RNA) TIMINA (T)TIMINA (T) (DNA)(DNA) URACILO (U)URACILO (U) (RNA)(RNA)
- 14. Posición de sustituyentesPosición de sustituyentes - NH- NH22 =O=O -CH-CH33 AA 66 CC 44 22 UU 2 y 42 y 4 GG 22 66 TT 2 y 42 y 4 55
- 15. Propiedades fisicoquímicasPropiedades fisicoquímicas Existencia de DipolosExistencia de Dipolos Posibilidad de puentes de hidrogenoPosibilidad de puentes de hidrogeno HidrofobicidadHidrofobicidad Anillos aromáticosAnillos aromáticos Pocos solubles en aguaPocos solubles en agua Interacción hidrofóbica de apilamientoInteracción hidrofóbica de apilamiento Disposición coplanar de los anillosDisposición coplanar de los anillos Tautomería o isemería dinámicaTautomería o isemería dinámica TAREA
- 16. Tautomería DinámicaTautomería Dinámica Tautomería ceto-enólicaTautomería ceto-enólica Tautomería imina-amina primariaTautomería imina-amina primaria
- 17. TautormeríaTautormería Lactima e imina 100.000 veces menosLactima e imina 100.000 veces menos abundantes que lactama y aminaabundantes que lactama y amina
- 18. Frecuente fuente de error en el ADNFrecuente fuente de error en el ADN
- 23. O N N N N NH2 OHOH CH2OP- O O O- H H H Pentosa Base NucleósidoFosfato Nucleótido Enlace N-glicosídico
- 24. NucleósidosNucleósidos Nucleósidos purínicos Sufijo –osinaNucleósidos purínicos Sufijo –osina AdenosinaAdenosina GuanosinaGuanosina Nucleósidos pimirmidínicos sufijo – idinaNucleósidos pimirmidínicos sufijo – idina CitidinaCitidina TimidinaTimidina UridinaUridina
- 25. NucleótidosNucleótidos Propiedades fisicoquímicasPropiedades fisicoquímicas Marcado carácter ácido debido a los gruposMarcado carácter ácido debido a los grupos fosfato.fosfato. Gran afinidad por cationes divalentes comoGran afinidad por cationes divalentes como MgMg2+2+ , Mn, Mn2+2+ y Cay Ca2+2+ Los NTPs y NDPs no existen como anionesLos NTPs y NDPs no existen como aniones libre, sino formando quelatos principalmentelibre, sino formando quelatos principalmente con Mgcon Mg2+2+
- 26. DNA Y RNADNA Y RNA Ácido fosfóricoÁcido fosfórico - Une los nucleótidos entre sí asociando- Une los nucleótidos entre sí asociando las pentosas de dos nucleótidoslas pentosas de dos nucleótidos consecutivosconsecutivos - La unión se produce con el carbono 3’- La unión se produce con el carbono 3’ de un nucleósido con el carbono 5’ delde un nucleósido con el carbono 5’ del siguientesiguiente
- 30. ADN – ARNADN – ARN DiferenciasDiferencias
- 31. Niveles estructuralesNiveles estructurales Estructura primariaEstructura primaria Representación detallada Representaciones esquemáticas pApCpG…. pACG…. ACG…. Representaciones abreviadas
- 32. Niveles estructuralesNiveles estructurales Estructura secundariaEstructura secundaria
- 33. Niveles estructuralesNiveles estructurales Estructura de orden superiorEstructura de orden superior
- 34. ADN y ARNADN y ARN Tipos de A. nucleicosTipos de A. nucleicos ARNARN ADNADN MonómeroMonómero RibonucleótidosRibonucleótidos DesoxirribonucleótidosDesoxirribonucleótidos FosfatosFosfatos Enlace fosfodiésterEnlace fosfodiéster AzúcarAzúcar RibosaRibosa DesoxiribosaDesoxiribosa PurinasPurinas Adenina, guaninaAdenina, guanina PirimidinasPirimidinas CitosinaCitosina UraciloUracilo TiminaTimina Componentes delmonómero
- 35. Propiedades fisicoquímicasPropiedades fisicoquímicas Propiedades en disoluciónPropiedades en disolución Las cadenas son hidrofílicasLas cadenas son hidrofílicas AcidosAcidos PolianionesPolianiones Se estabilizan por unión a proteínas..Se estabilizan por unión a proteínas.. Gran viscosidadGran viscosidad
- 36. Propiedades fisicoquímicasPropiedades fisicoquímicas ReacitvidadReacitvidad ADNADN ARNARN E. fosfodiesterE. fosfodiester E. N-glicosidicoE. N-glicosidico E. fosfodiesterE. fosfodiester E. N-glicosidicoE. N-glicosidico Medio Acido fuerteMedio Acido fuerte SiSi SiSi SiSi SiSi Medio Acido debilMedio Acido debil NoNo SiSi (purinas(purinas especialmente)especialmente) NoNo SiSi (purinas(purinas especialmente)especialmente) Medio alcalinoMedio alcalino NoNo NoNo SiSi NoNo
- 37. Propiedades fisicoquímicasPropiedades fisicoquímicas ReacitvidadReacitvidad
- 39. Propiedades fisicoquímicasPropiedades fisicoquímicas Absorción UVAbsorción UV
- 40. DNADNA Perth, Australia Life Science, UC Davis Chambord, France
- 42. Modelo De WATSON-CRICKModelo De WATSON-CRICK Cada molécula de DNA está formada por dosCada molécula de DNA está formada por dos largas cadenas de polinucleótidos que correnlargas cadenas de polinucleótidos que corren en direcciones opuestas formando una héliceen direcciones opuestas formando una hélice doble alrededor de un eje imaginario central.doble alrededor de un eje imaginario central. De esta forma la polaridad de cada cadenaDe esta forma la polaridad de cada cadena es opuestaes opuesta Cada nucleótido está en un planoCada nucleótido está en un plano perpendicular al de la cadena polinucleótidaperpendicular al de la cadena polinucleótida
- 43. Modelo De WATSON-CRICKModelo De WATSON-CRICK 5’ 3’ 3’ 5’ Cada una de las dos hélices es un polinucleótido entrelazado con el otro de manera que su polaridad es opuesta (es decir, corren en sentido antiparalelo)
- 44. Modelo De WATSON-CRICKModelo De WATSON-CRICK
- 45. Modelo De WATSON-CRICKModelo De WATSON-CRICK Las dos cadenas se encuentran apareadasLas dos cadenas se encuentran apareadas por uniones de hidrógeno establecidas entrepor uniones de hidrógeno establecidas entre los pares de baseslos pares de bases El apareamiento es altamente específico.El apareamiento es altamente específico. Existe una distancia física de 11Existe una distancia física de 11 ÅÅ entre dosentre dos moléculas de desoxirribosa en las cadenasmoléculas de desoxirribosa en las cadenas opuestasopuestas Sólo se pueden aparear una base púrica conSólo se pueden aparear una base púrica con una pirimídica. A-T G-Cuna pirimídica. A-T G-C Entre A y T hay dos puentes de hidrógeno yEntre A y T hay dos puentes de hidrógeno y entre G-C hay tres.entre G-C hay tres. Son imposibles otras uniones.Son imposibles otras uniones.
- 46. Modelo de Watson y CrickModelo de Watson y Crick Complementariedad de las bases nitrogenadasComplementariedad de las bases nitrogenadas
- 48. Modelo De WATSON-CRICKModelo De WATSON-CRICK La secuencia axail de bases a lo largoLa secuencia axail de bases a lo largo de una cadena de polinucleótidosde una cadena de polinucleótidos puede variar considerablemente, peropuede variar considerablemente, pero en la otra cadena la frecuencia debeen la otra cadena la frecuencia debe ser complementariaser complementaria
- 50. Estructura de DNAEstructura de DNA
- 51. RNARNA La estructura primaria es similar a la del DNA peroLa estructura primaria es similar a la del DNA pero Las bases nitrogenadas La Timina (T) ribosaLa desoxirribosa Uracilo (U)
- 52. RNARNA Tres tipos de RNATres tipos de RNA Ribosómico Mensajero Transferencia o soluble -Constituido por ribonucleótidos (nucleótidos de ribosa) -Los ribonucleótidos se unen entre sí, igual que en el DNA, a través de un ácido fosfórico en sentido 5’3’ -El RNA es casi siempre monocatenario
- 53. RNARNA Los distintos tipos de RNA permiten laLos distintos tipos de RNA permiten la expresión fenotípica del DNAexpresión fenotípica del DNA:: Como mensaje genético que determinaComo mensaje genético que determina la secuencia de aminoácidos en lala secuencia de aminoácidos en la síntesis de proteína:síntesis de proteína: RNA mensajeroRNA mensajero oo mRNAmRNA
- 54. RNARNA Como molécula que activa a losComo molécula que activa a los aminoácidos para poder seraminoácidos para poder ser incorporados en una nueva proteína:incorporados en una nueva proteína: RNA de transferencia o tRNARNA de transferencia o tRNA Como elemento estructural básico deComo elemento estructural básico de las partículas encargadas de llevar alas partículas encargadas de llevar a cabo la síntesis proteica, los ribosomas:cabo la síntesis proteica, los ribosomas: RNA ribosómico o rRNARNA ribosómico o rRNA
- 55. Hélices levógiras y dextrógiras
- 56. DIMENSIONESDIMENSIONES DEL ADNDEL ADN Surco Menor Surco Mayor
- 59. Dos surcos de igual tamaño se crearían si las bases se unen en forma simétrica con el esqueleto azúcar-fosfato Porque hay un surco mayor y menor en el ADN? Las bases se unen en forma asimétrica al esqueleto del azúcar- fosfato formando los dos surcos de tamaño desigual.
- 60. Surco mayor y menor en el ADN
- 61. Surco mayor Surco menor Surco menor Surco mayor
- 65. Niveles estructuralesNiveles estructurales Estructura de orden superiorEstructura de orden superior
- 66. Condensación o EmpaquetamientoCondensación o Empaquetamiento NucleosomasNucleosomas SolenoideSolenoide EucromatinaEucromatina HeterocromatinaHeterocromatina CromosomaCromosoma
- 67. NucleosomaNucleosoma Unidades de núcleoproUnidades de núcleopro teínas formadas cada unateínas formadas cada una por un cilindro corto depor un cilindro corto de histonas en forma de discohistonas en forma de disco envuelto en ácido nucléico.envuelto en ácido nucléico. Formado por 8 moléculasFormado por 8 moléculas de histonas conocidasde histonas conocidas como H2A, H2B, H3 y H4.como H2A, H2B, H3 y H4.
- 69. SolenoideSolenoide Anillos circulares yAnillos circulares y continuos formadoscontinuos formados cada uno por seiscada uno por seis nucleosomasnucleosomas
- 71. CromatinaCromatina Filamento de DNA yFilamento de DNA y proteínasproteínas
- 73. CromosomasCromosomas Estructuras de variasEstructuras de varias formas y tamañosformas y tamaños formada porformada por nucleoproteínasnucleoproteínas.. NucleoproteínasNucleoproteínas –– combinación de ácidocombinación de ácido nucléico y proteínasnucléico y proteínas (histonas)(histonas) Formada por una ó dosFormada por una ó dos cromátidas (hermanas),cromátidas (hermanas), unidas por un centrómerounidas por un centrómero (DNA no está contraído).(DNA no está contraído).
- 74. Superenrrollamiento ySuperenrrollamiento y Topología del ADNTopología del ADN Parte de laParte de la condensación secondensación se logra con ellogra con el superenrrollamientosuperenrrollamiento Contribuye a explicarContribuye a explicar como unacomo una macromoléculamacromolécula puede alojarse en lapuede alojarse en la célulacélula
- 75. Se define al giro o retorcimiento del DNASe define al giro o retorcimiento del DNA sobre sí mismasobre sí misma DNADNA TamañoTamaño Longitud enLongitud en forma B-forma B- DNADNA Dimensiones deDimensiones de compactacióncompactación E. ColiE. Coli 4.7 104.7 1066 pbpb 1,6 mm1,6 mm 2 um2 um CadaCada CromosomaCromosoma HumanoHumano 50 – 250 1050 – 250 1066 pbpb 17 – 8517 – 85 mmmm 4-6 um4-6 um Genoma HumanoGenoma Humano diploidediploide 6,6 106,6 1099 pbpb 2,2 metros2,2 metros 4-6 um4-6 um Superenrrollamiento del DNASuperenrrollamiento del DNA
- 76. El superenrrollamiento es mas conocido yEl superenrrollamiento es mas conocido y mejor comprendido en ADN circularmejor comprendido en ADN circular ProcariotasProcariotas MitocondriasMitocondrias CloroplastosCloroplastos
- 77. ConformacionesConformaciones Conformación relajadaConformación relajada No superenrrolladoNo superenrrollado EstableEstable Conformación adoptadaConformación adoptada por el DNA en su forma Bpor el DNA en su forma B Ejemplo (Luque)Ejemplo (Luque) ADN circularADN circular 210 pb210 pb 20 vueltas de helice20 vueltas de helice 10,5 pb por vuelta10,5 pb por vuelta
- 78. ConformacionesConformaciones Conformación superenrrolladasConformación superenrrolladas SuperenrrolladoSuperenrrollado No EstableNo Estable No relajadoNo relajado Se produce por disminución o aumento en elSe produce por disminución o aumento en el numero de vueltas de hélicenumero de vueltas de hélice Adopta formaciones diferentes al B-DNAAdopta formaciones diferentes al B-DNA La tensión se contrarresta mediante laLa tensión se contrarresta mediante la formación de un superenrollamientoformación de un superenrollamiento
- 79. Superenrollamiento negativoSuperenrollamiento negativo Si se reduce en nro deSi se reduce en nro de vueltas de hélice, lavueltas de hélice, la tensión se libera formandotensión se libera formando una superhelice que se leuna superhelice que se le asigna un valor negativoasigna un valor negativo de superenrrollamientode superenrrollamiento Ejemplo (Luque)Ejemplo (Luque) ADN circularADN circular 210 pb210 pb 19 vueltas de helice19 vueltas de helice 11,1 pb por vuelta11,1 pb por vuelta
- 80. Superenrollamiento positivoSuperenrollamiento positivo Si se aumenta en nro deSi se aumenta en nro de vueltas de hélice, lavueltas de hélice, la tensión se libera formandotensión se libera formando una superhelice que se leuna superhelice que se le asigna un valor positivo deasigna un valor positivo de superenrrollamientosuperenrrollamiento Ejemplo (Luque)Ejemplo (Luque) ADN circularADN circular 210 pb210 pb 21 vueltas de helice21 vueltas de helice 10 pb por vuelta10 pb por vuelta
- 82. TopologíaTopología Rama de las matemáticas que estudia lasRama de las matemáticas que estudia las propiedades de posición relativa de laspropiedades de posición relativa de las partes de un objetopartes de un objeto Numero de enlace (Numero de enlace (L o Lk) nº de veces) nº de veces que las hebras se cruzan entre si.que las hebras se cruzan entre si.
- 83. L = 0 las dos hebras estan físicamenteL = 0 las dos hebras estan físicamente separadasseparadas LL ≠ 0 las hebras estan físicamente≠ 0 las hebras estan físicamente “ligadas”“ligadas” Para B-DNA L es positivo por serPara B-DNA L es positivo por ser dextrógiradextrógira Los superenrrollamientos surgen porLos superenrrollamientos surgen por cambios en Lcambios en L
- 84. Valor del superenrrollamientoValor del superenrrollamiento Diferencia de L (estado relajado) y LDiferencia de L (estado relajado) y L (superenrrollado)(superenrrollado) EjemploEjemplo 210 pb/ 10,5 pb por vuelta = 20 vueltas de helice210 pb/ 10,5 pb por vuelta = 20 vueltas de helice L= 20L= 20 L = 18 Superenrrollamiento= 18 – 20 = -2 L = 22 Superenrrollamiento= 22 – 20 = +2
- 85. ADN - TiposADN - Tipos
- 86. ADN – A ADN – B ADN - Z
- 91. DNA Structures: A, B and Z
- 92. Conformación delConformación del azúcarazúcar
- 93. Conformación de los NucleotidosConformación de los Nucleotidos Existen dos tipos de orientaciones Alrededor del enlace N-glicosídico Estan conformaciones son identificadas como syn y anti. La conformación anti es la predominante
- 94. A B Z Forma y Tamaño Ancha y corta Intermedia Estrecha y larga Giro Dextro Dextro Levo Grosor 25,5 Å 23,7 Å 18,4 Å Dist e/bases 2.3 Å 3.4 Å 3.8 Å Bases/vuelta 11 10.4 12 Pares de base por vuelta 25,3 Å 35,4 Å 45,6 Å Rotación 32,7º 35,4º 45,6º Inclinación 19º 1º 9º Surco Mayor Estrecho profundo Ancho profundidad media Plano Sin profundidad Surco Menor Amplio No profundo Estrecho profundidad media Estrecho Profundo Dribosa C3’-endo C2’-endo C2’ endo (C) C3’ endo (G) N-glicosidico anti anti anti (C) syn (G)
- 97. H - DNAH - DNA Regiones ricasRegiones ricas en pirimidinasen pirimidinas en una hebra yen una hebra y ricas en purinasricas en purinas en la otraen la otra PosiblePosible aplicación enaplicación en terapia génicaterapia génica de inhibición dede inhibición de la expresión.la expresión.
- 98. Una estructura tan bonita tenía, por fuerza, que existirUna estructura tan bonita tenía, por fuerza, que existir J. WatsonJ. Watson
Notas del editor
- La tarea es averiguar otras bases nitrogenadas de interes.. Se encuetra en el libro de Luque en la página 13