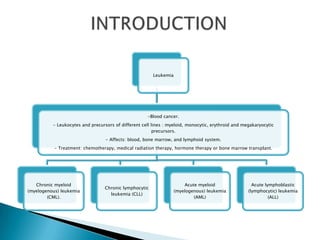
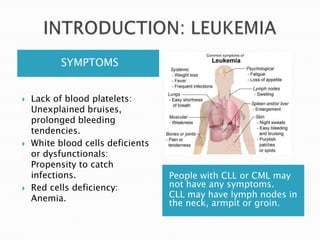
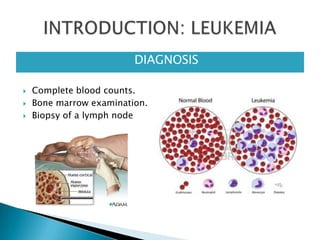
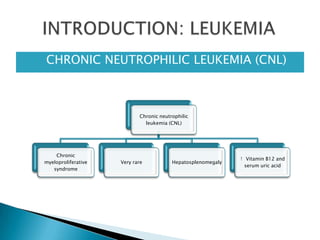
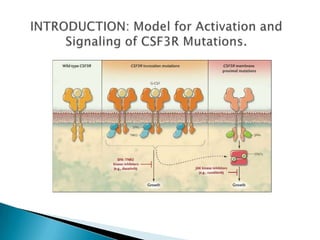
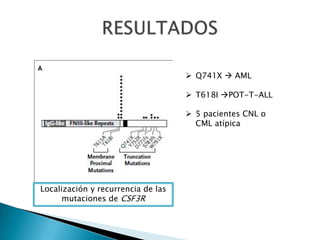
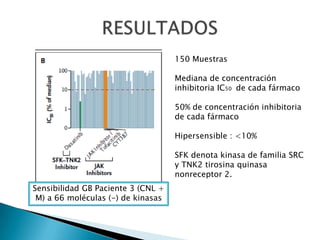
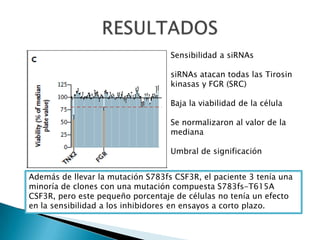
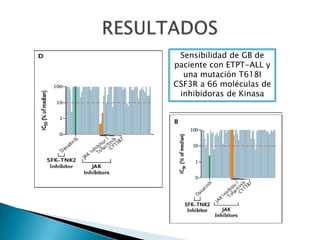
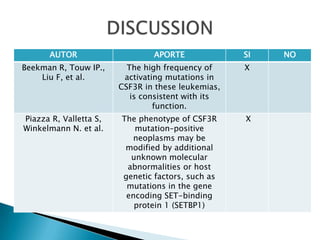
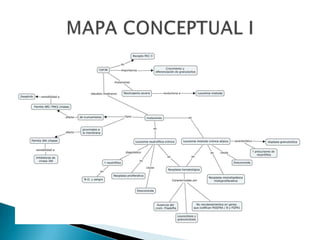
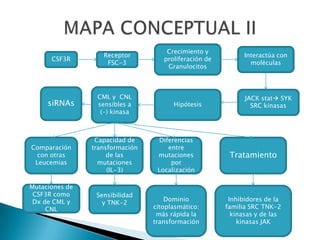
Este estudio investigó las mutaciones en el gen CSF3R en pacientes con leucemia crónica neutrofílica (CNL) y leucemia mieloide crónica atípica (aCML). Los resultados mostraron que las mutaciones en CSF3R definen estas enfermedades y pueden predecir la sensibilidad a inhibidores de quinasa. Las mutaciones proximales de membrana y de truncamiento en CSF3R transformaron células, lo que sugiere que estas mutaciones contribuyen a la patogénesis de CNL y aCML.