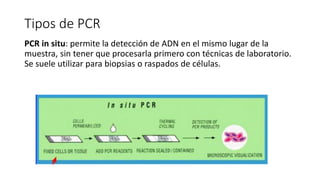
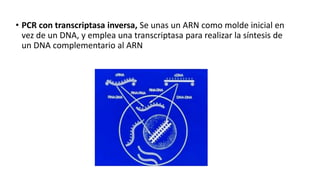
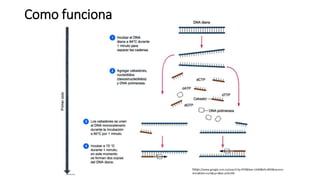
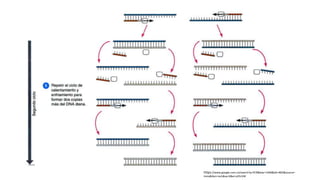
La PCR (reacción en cadena de la polimerasa) es una técnica que permite amplificar rápidamente muestras pequeñas de ADN. Utiliza cebadores y ADN polimerasa para crear miles de millones de copias de un fragmento de ADN en unas horas. Existen varios tipos de PCR como la PCR en tiempo real que cuantifica la cantidad de ADN inicial y la PCR anidada que amplifica muestras mínimas de ADN. Un estudio identificó Bordetella spp. como agente causal de tos ferina en muestras de Oaxaca